Ecología Molecular – 2014 – TP1
description
Transcript of Ecología Molecular – 2014 – TP1

Ecología Molecular – 2015 – TP1
Marcadores moleculares

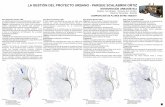
Región de Control (D-loop) del ADN mitocondrial del jurel Trachurus murphyi

- un azúcar de 5 carbonos – desoxirribosa- fosfato - uniones entre los azúcares- bases: purinas = adenina y guanina pirimidinas = timina y citosina

Muestreo

1. Extracción
2. Amplificación¿Y los partidores?


1 2
¿Existen secuencias de la D-loop de Trachurus murphyi?
3

1


1 2
Diseñar sus partidores propios:¿Existe una secuencia del genoma mitocondrial del género?

1

1

1

1



Busqueda de los partidores

1. Extracción
2. Amplificación
3. Secuenciación

H
L
AA C A C
T T G T G
T T G T G
AA C A C
AA C A C
GT G T T
AA C A C
T T G T G
AA C A C
AA C A C
R
F
5' 3'
5'3'
5' 3'

importar JREL2-TRNA-F.ab1
PROcessor of SEQuences (ProSeq)
(c) 1999 - 2007 by Dmitry Filatov,
http://www.biology.ed.ac.uk/research/institutes/evolution/software/filatov/proseq.htm




H
L
AA C A C
T T G T G
AA C A CF
5' 3'
5'3'

H



importar JREL2-TRNA-R.ab1

AA C A C
GT G T T



AA C A C
GT G T T
5' 3'
5' 3'
AA C A C
T T G T G5'3'
5' 3'
Reverse
AA C A C
AA C A C5'3'
5' 3'
Complemente

Emsamblar secuencias:
JREL12-TRNA-F.ab1 con JREL2-TRNA-R.ab1
1. Invertir la secuencia complementaria
2. sobreponer
3. fusionar



Alineamiento de las secuencias F y R
I Insertar un espacio

I Insertar un espacio
Eliminar base(s)

Alineamiento de secuencias
1. Importar todas las secuencias F
2. Alinear
3. Cortar las extremidades
4. Verificar cada mutación






Pero ustedes tienen esto…
Y luego de alinear (ctrI)

Y del otro lado…
Cortar las extremidades
Revisar las secuencias alignadas

Polimorfismo


Aprob
ado

Estadísticas para caracterizar la variación del ADN
1) Número de sitios polimórficos S
2) Número de alelos diferentes (haplotipos) K
3) Diversidad H = 1 - pi2 (pi
2 : frecuencia del haplotipo i)
4) Número promedio de diferencias entre 2 secuencias

Abrir jurel.nex

Calcular los índices de diversidad (S, K, H, Π)
1

1


Abrir el archivo: Jurel1pop.arp
1

13
2

3
1
2


Secuencias Fabiola
1. ¿Qué son estas secuencias? (organismo, gen)
1. ¿Existe sitios variables entre estos individuos?
1. ¿Algo que comentar…?


AAAACAATGAAAAGAATG

¿Genotipos para cada individuos?

ARD4 TG/TG
ARD5 CC/CC
ARD6 TG/CC – TC/CG
ARD16 CC/CG
Solución más parsimoniosa
3 haplotipos

Microsatélites o SSR
(Single Sequence Repeats)

Locus Motivo repetido Tamaño del alelo
7F12 (AC)29180 bp
7D3 (AG)4AT(AG)12276 bp







Frecuencias alélicas e índices de diversidad
Abrir el archivo: micro1pop.gtx

1
2
3

1